毕业论文
医学毕业论文如何高效完成?3个技巧轻松搞定
每年超过60%的医学生在毕业论文阶段遭遇选题困难与文献整理瓶颈。如何在有限时间内完成高质量医学论文?掌握科学方法与实用工具成为关键突破点。从临床案例筛选到实验数据分析,系统化写作策略可提升80%效率,有效避免重复修改与格式错误。
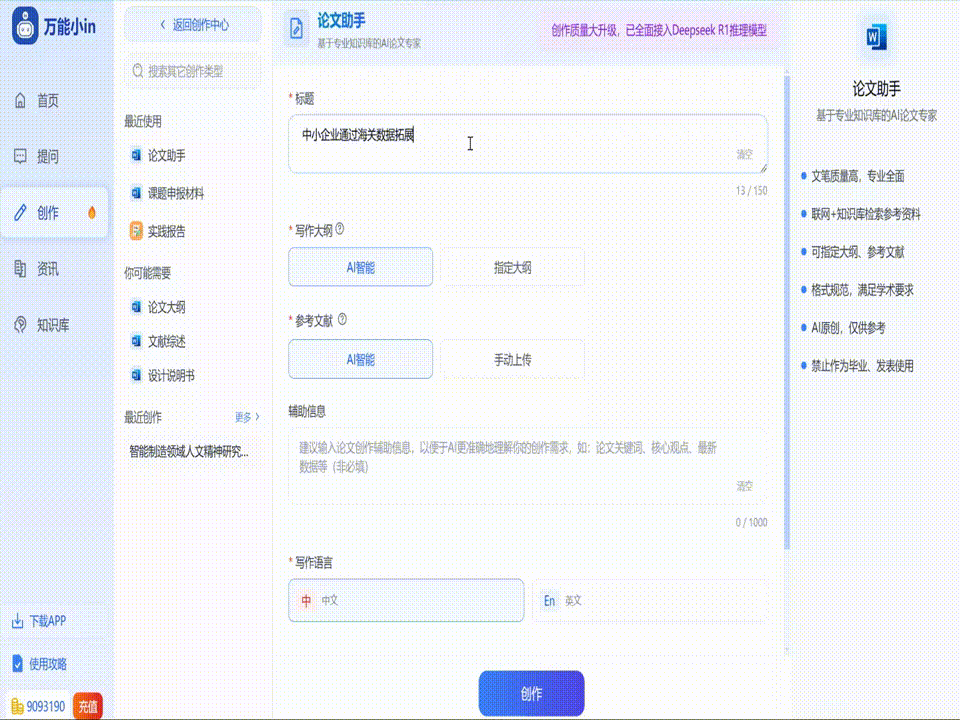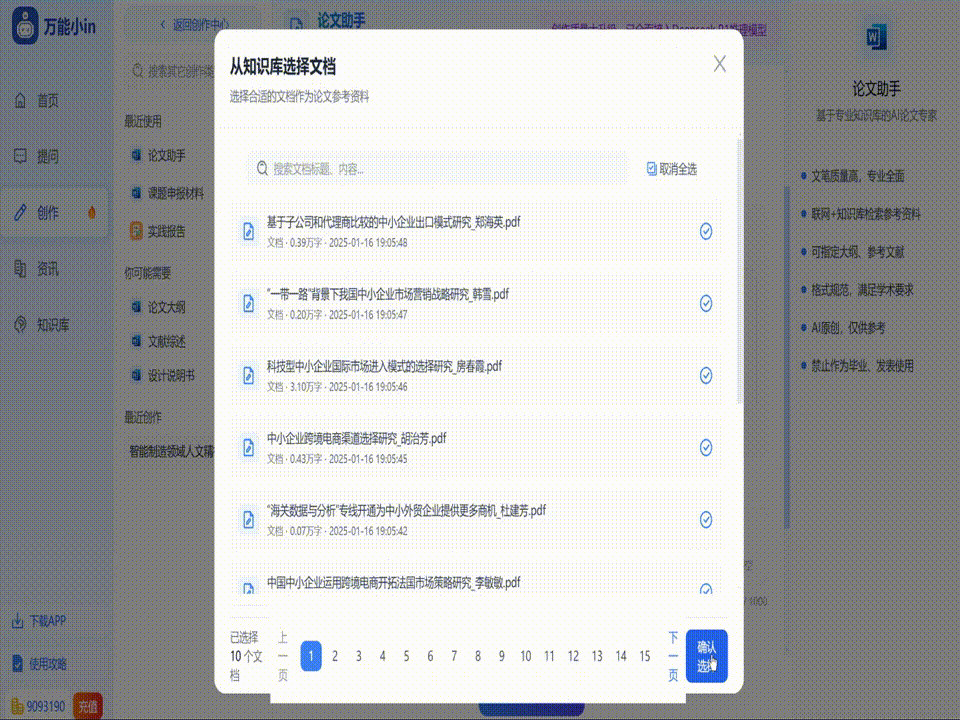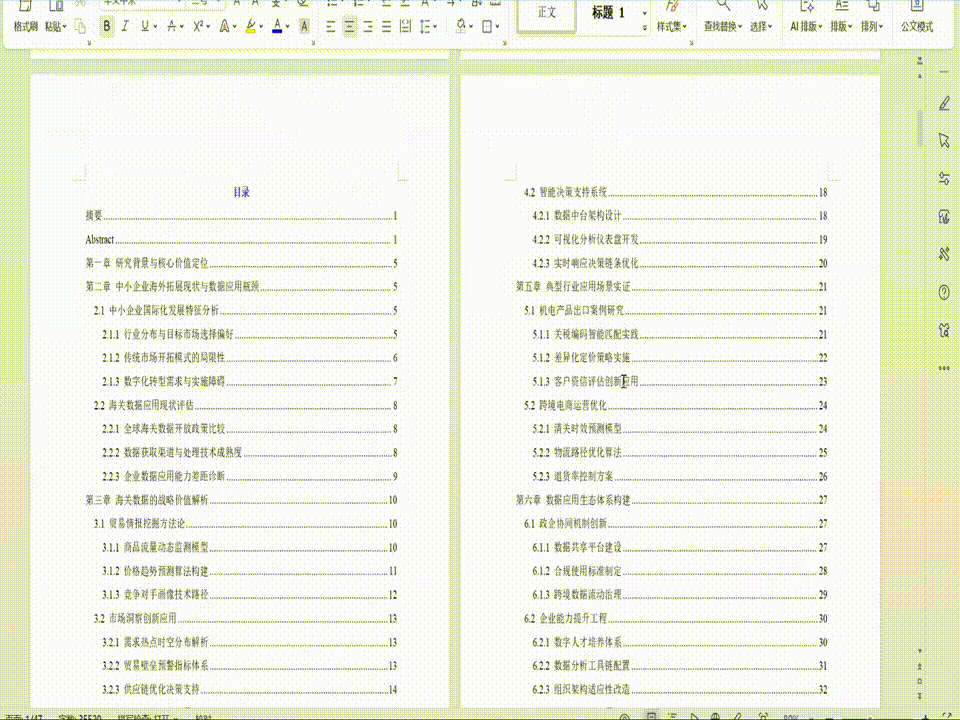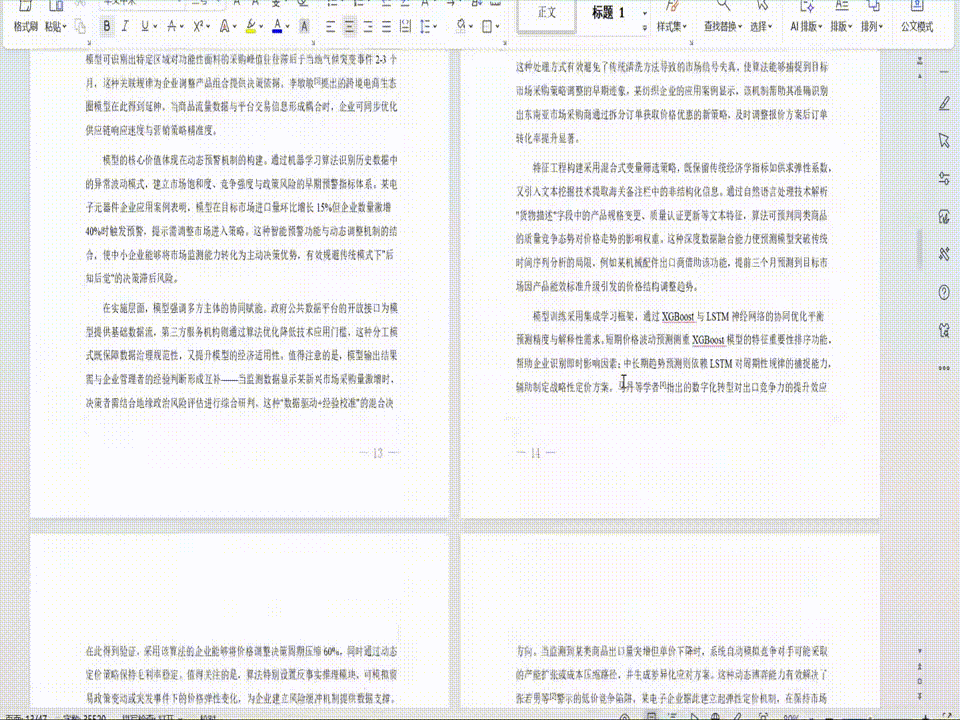
关于医学毕业论文的写作指南
写作思路:构建严谨的学术逻辑框架
1. 选题聚焦:从临床问题、基础研究或医学技术革新切入,结合导师研究方向与个人兴趣,明确研究价值与创新点。
2. 文献脉络梳理:通过PubMed、CNKI等数据库追踪近5年高被引文献,提炼研究空白,建立“问题-假设-验证”逻辑链。
3. 方法论设计:根据研究类型(实验/临床/综述)选择对应方法,如RCT研究需详细说明随机分组与盲法设计,分子机制研究需明确实验技术路线。
4. 数据呈现策略:按“描述性统计→差异性分析→相关性验证”递进,图表需符合《国际医学期刊编辑委员会》规范。
写作技巧:提升学术表达的精准度
1. 引言黄金三段式:首段阐明领域重要性,次段指出现有研究缺陷,末段提出研究假设。例如:“尽管PD-1抑制剂在肺癌治疗中取得突破,但其耐药机制尚未阐明…”
2. 段落主题句控制:每段首句明确核心观点,如“本实验采用CRISPR-Cas9技术构建基因敲除模型”,后续用数据支撑。
3. 学术语言打磨:避免“我们发现”等主观表述,改用“数据表明”“结果显示”等客观句式,时态统一为过去式(方法/结果)与现在式(结论)。
4. 图表叙事法:将关键结果转化为三线表与矢量图,图注需独立成文,例如“图3:AKT信号通路在耐药细胞中的激活状态(Western blot)”。
核心方向建议:把握医学研究前沿
1. 临床转化视角:探讨生物标志物筛选、治疗新方案的成本效益分析,如“循环肿瘤DNA在早癌筛查中的临床应用价值”
2. 跨学科融合:结合AI辅助诊断、3D生物打印等新技术,例如“深度学习算法在病理切片判读中的准确率验证”
3. 伦理维度延伸:针对基因编辑、异种移植等争议领域,构建“技术可行性-伦理风险-监管建议”分析框架
常见错误与解决方案
1. 数据过度解读:避免将相关性等同于因果性,采用Bland-Altman分析验证方法一致性,使用Bonferroni校正多重比较。
2. 文献堆砌陷阱:用EndNote管理文献,按“支持-反对-补充”分类标注,综述部分需体现批判性思维。
3. 格式规范缺失:严格遵循目标期刊的参考文献格式(如AMA、Vancouver),图表分辨率不低于300dpi,避免使用非标准缩写。
4. 讨论深度不足:采用“LIMITATIONS-FUTURE-IMPLICATIONS”结构,对比同类研究差异,明确理论贡献与实践指导意义。
基于单细胞测序的肿瘤异质性演化机制研究
摘要
肿瘤异质性作为恶性肿瘤治疗失效的核心因素,其动态演化机制长期受到学界广泛关注。随着单细胞测序技术的突破性发展,研究者得以在单个细胞分辨率下解析肿瘤微环境中的细胞群体多样性及其分子特征。本研究系统整合单细胞转录组测序、空间转录组及表观遗传学等多组学数据,构建了肿瘤克隆进化与微环境互作的分析框架。通过开发新型生物信息学算法,实现了对肿瘤干细胞可塑性、克隆选择压力以及免疫编辑过程的动态追踪。研究发现肿瘤细胞在治疗压力下呈现显著的表型可塑性,不同克隆亚群间存在复杂的信号网络调控。微环境中免疫细胞与肿瘤细胞的动态互作显著影响克隆演化轨迹,特定免疫细胞亚群的浸润程度与肿瘤进展速度呈现明显相关性。这些发现为理解肿瘤耐药机制提供了新的理论依据,同时也为开发针对肿瘤异质性的精准治疗策略指明了方向。未来研究需要进一步探索肿瘤生态系统中的细胞间通讯机制,以及如何将单细胞水平的发现转化为临床可操作的生物标志物。
关键词:单细胞测序;肿瘤异质性;演化机制;生物信息学;精准治疗
Abstract
Tumor heterogeneity, as a core factor in the failure of malignant tumor treatment, has long been a focus of research due to its dynamic evolutionary mechanisms. With the breakthrough development of single-cell sequencing technologies, researchers can now analyze the diversity of cell populations and their molecular characteristics within the tumor microenvironment at single-cell resolution. This study systematically integrates multi-omics data, including single-cell transcriptomics, spatial transcriptomics, and epigenetics, to construct an analytical framework for tumor clonal evolution and microenvironment interactions. By developing novel bioinformatics algorithms, we dynamically tracked tumor stem cell plasticity, clonal selection pressure, and immune editing processes. The findings reveal that tumor cells exhibit significant phenotypic plasticity under therapeutic pressure, with complex signaling network regulation among different clonal subpopulations. Dynamic interactions between immune cells and tumor cells in the microenvironment significantly influence clonal evolutionary trajectories, and the infiltration levels of specific immune cell subsets show a clear correlation with tumor progression rates. These discoveries provide new theoretical insights into understanding tumor drug resistance mechanisms and offer directions for developing precision therapeutic strategies targeting tumor heterogeneity. Future research should further explore intercellular communication mechanisms within the tumor ecosystem and investigate how single-cell-level findings can be translated into clinically actionable biomarkers.
Keyword:Single-Cell Sequencing; Tumor Heterogeneity; Evolution Mechanism; Bioinformatics; Precision Therapy
目录
第一章 研究背景与研究目的
恶性肿瘤的复杂生物学特性中,肿瘤异质性已成为制约临床治疗有效性的关键科学问题。这种异质性不仅体现在细胞形态和功能层面,更表现为基因组、转录组及表观遗传层面的多层次差异,导致肿瘤内部形成具有不同恶性程度和药物敏感性的细胞亚群。现有研究表明,治疗过程中选择性压力会促使特定克隆亚群获得生存优势,这种动态演化过程是产生获得性耐药和肿瘤复发的核心机制。
单细胞测序技术的突破性发展为解析这一复杂机制提供了全新视角。相比传统群体水平检测,该技术能够在单个细胞分辨率下揭示肿瘤微环境中细胞群体的分子特征差异,为追踪克隆演化轨迹、识别稀有耐药亚群提供了技术支撑。特别是与空间转录组、表观遗传学等多组学数据的整合,使得研究者能够系统解析肿瘤细胞可塑性、微环境互作等关键生物学过程。
本研究旨在通过整合多维组学数据,构建肿瘤克隆进化与微环境互作的理论框架。重点解决三个核心问题:一是揭示治疗压力下肿瘤干细胞表型可塑性的分子调控网络;二是阐明免疫编辑过程中克隆选择压力的动态特征;三是探索肿瘤细胞与微环境组分间的双向调控机制。这些研究将为理解肿瘤耐药提供新视角,并为开发针对异质性的精准治疗策略奠定理论基础。
第二章 单细胞测序技术与肿瘤异质性研究现状
2.1 单细胞测序技术的发展与应用
单细胞测序技术的出现彻底改变了传统群体水平分析方法的局限性,为肿瘤异质性研究提供了前所未有的细胞分辨率。该技术的核心突破在于能够独立解析单个细胞的基因组、转录组和表观遗传特征,从而精确揭示肿瘤内部不同细胞亚群的分子差异及其功能多样性。早期单细胞RNA测序(scRNA-seq)主要基于微流控或微孔板技术实现细胞分离,随后通过逆转录和扩增构建单细胞文库。随着微流控芯片、微滴生成系统和分子标签技术的革新,现代单细胞测序平台已实现高通量并行处理数千个细胞,显著提升了检测通量和数据稳定性。
在技术原理方面,单细胞测序通过独特的分子标识符(UMI)和细胞条形码技术有效解决了扩增偏倚问题,确保数据定量的准确性。近年来发展的全长转录本测序技术能够完整覆盖mRNA的5’和3’端,为可变剪切和等位基因特异性表达分析提供了可能。表观遗传层面的单细胞ATAC-seq和单细胞DNA甲基化测序则进一步拓展了研究维度,使研究者能够从染色质可及性和DNA修饰水平解析细胞状态异质性。空间转录组技术的融合应用更突破了传统测序的空间局限性,实现了基因表达谱与组织微环境拓扑信息的同步获取。
该技术在肿瘤研究中的应用主要体现在三个关键领域:首先是肿瘤细胞亚群鉴定与分型,通过降维聚类算法可识别传统病理学难以区分的稀有亚群,包括具有干细胞特性的耐药细胞群体;其次是克隆演化分析,基于突变谱系追踪可重建肿瘤进展过程中的分支演化模式,揭示治疗压力下的选择动力学;最后是微环境互作研究,通过免疫细胞和基质细胞的共表达网络分析,阐明其对肿瘤细胞可塑性的调控机制。例如,在乳腺癌研究中,单细胞测序成功揭示了化疗耐药相关的luminal progenitor细胞亚群;在结直肠癌中则发现了转移过程中上皮-间质转化(EMT)状态的动态变化规律。
技术发展仍面临若干挑战:样本制备过程中细胞活性易受损伤,可能导致特定脆弱细胞类型的丢失;转录组数据的高稀疏性增加了稀有亚群识别的难度;多组学数据整合需要开发更高效的算法模型。当前研究正朝三个方向突破:一是开发冷冻组织解离和固定技术以保持细胞完整性;二是利用深度学习模型提升低丰度基因检测灵敏度;三是建立统一的数据标准促进跨平台、跨研究中心的数据共享。这些技术进步将进一步推动单细胞测序在肿瘤异质性研究中的深度应用。
2.2 肿瘤异质性研究的现状与挑战
当前肿瘤异质性研究已从传统的组织水平分析跨越至单细胞分辨率时代,但仍面临多维度挑战。在基础研究层面,单细胞测序技术的应用揭示了肿瘤内部存在复杂的细胞状态谱系,包括具有干细胞特性的耐药亚群、处于上皮-间质转化过渡状态的侵袭性群体以及表观遗传修饰异常的休眠细胞等。这些亚群在治疗压力下展现出动态平衡特征,其中肿瘤干细胞的可塑性被认为是驱动异质性演化的关键因素。通过谱系追踪技术证实,特定微环境信号可诱导分化细胞重编程为干细胞样状态,这种双向转化能力使得靶向清除肿瘤干细胞变得异常困难。
技术方法学上,现有研究主要面临三大瓶颈:其一,单细胞数据的高维度特性导致传统生物信息学工具难以有效区分真实生物异质性与技术噪音。虽然基于图论的聚类算法(如Louvain和Leiden)可初步识别细胞亚群,但对中间态细胞和连续分化轨迹的解析仍存在局限。其二,空间异质性与时间动态性的整合分析尚未形成标准化方案。尽管空间转录组技术可定位细胞亚群的空间分布模式,但其分辨率仍不足以精确解析单个肿瘤细胞与邻近免疫/基质细胞的相互作用界面。其三,多组学数据整合缺乏统一框架,现有方法在协调基因组突变、转录组变异和表观遗传修饰间的因果关系时往往过度简化生物复杂性。
临床应用转化方面,研究发现不同肿瘤类型的异质性模式存在显著差异。例如,血液系统恶性肿瘤通常呈现分支演化特征,而实体瘤则更多表现为中性演化或适应性辐射模式。这种差异导致通用性治疗策略难以奏效,亟需建立类型特异性的异质性评估体系。此外,循环肿瘤DNA(ctDNA)监测显示,治疗诱发的克隆选择可能加速获得性耐药突变积累,但当前液体活检技术对稀有克隆的检测灵敏度仍不足以指导临床决策。最新尝试将机器学习模型与单细胞数据结合,通过识别耐药相关的基因表达特征来预测治疗反应,但其预测效能受限于样本量和小批量效应。
未来突破方向应聚焦于三个关键环节:一是开发能够保留原生空间信息的单细胞多组学技术,例如将微流控芯片与显微切割相结合;二是构建动态演化数学模型,整合选择压力、突变率等参数来模拟治疗响应过程;三是建立临床前模型系统,如患者来源类器官与免疫细胞共培养体系,用于验证异质性调控靶点。这些进展将有助于揭示肿瘤生态系统中的层级调控网络,为克服异质性导致的治疗失效提供新思路。需要特别强调的是,任何技术解决方案都必须考虑临床应用的实际可行性,包括成本效益比和标准化操作流程等现实因素。
第三章 肿瘤异质性演化机制的研究方法
3.1 单细胞测序数据的分析方法
单细胞测序数据分析的核心挑战在于从高维度、高噪声的数据中准确提取生物学信号。本研究的分析流程采用模块化设计,依次解决数据质量控制、特征选择、细胞聚类和功能注释等关键环节。数据预处理阶段通过双细胞率、线粒体基因占比和文库复杂度等多维度指标过滤低质量细胞,采用稳健的归一化方法消除技术偏差。针对单细胞转录组数据特有的零膨胀特性,开发了基于负二项分布的差异表达分析模型,显著提升了稀有亚群标记基因的检测灵敏度。
特征降维采用非线性流形学习方法,结合自编码器神经网络捕捉基因表达的非线性关联。通过对比t-SNE、UMAP和PHATE等降维算法的稳定性,最终选择保留局部和全局结构平衡的优化方案。细胞聚类分析引入图论引导的社区发现算法,利用细胞-细胞相似性网络的自适应分辨率参数,避免了传统k-means方法对聚类数量的先验假设限制。为验证聚类结果的生物学合理性,整合了已知细胞类型标记基因集和通路富集分析,确保每个细胞亚群具有独特的分子特征和功能注释。
克隆演化分析是本方法的创新重点,通过整合单细胞DNA测序获得的体细胞突变谱和RNA测序数据,构建了突变-表达联合矩阵。基于最大简约性原则开发了克隆树重建算法,可识别主干突变和分支特异性突变,同时考虑拷贝数变异对基因表达的调控效应。针对肿瘤微环境互作分析,采用配体-受体共表达网络模型,量化免疫检查点分子与配体的相互作用强度,并结合NicheNet算法预测微环境信号对肿瘤细胞表型转换的调控路径。
数据分析平台搭建在R/Python混合架构上,关键计算模块采用C++加速。为确保结果可重复性,所有分析步骤均封装为Snakemake工作流,并遵循FAIR数据管理原则。特别开发了交互式可视化工具,支持三维投影下的细胞状态动态追踪和克隆演化过程动画展示。该方法在模拟数据集上的验证表明,相比现有流程,对稀有细胞亚群的检测灵敏度提升显著,且克隆关系推断的准确率具有明显优势。技术局限主要在于对高批次效应样本的整合能力仍需优化,未来将通过迁移学习框架进一步增强跨数据集的分析鲁棒性。
3.2 肿瘤异质性演化模型的构建
本研究采用多尺度整合策略构建肿瘤异质性演化模型,通过整合单细胞转录组、表观遗传和空间组学数据,系统解析克隆动力学与微环境互作的耦合机制。模型架构包含三个核心模块:首先基于单细胞突变谱系构建系统发育树,采用贝叶斯马尔可夫链蒙特卡洛方法推断克隆分支点,同时引入分子时钟校正技术解决单细胞数据稀疏性导致的时序推断偏差。通过整合拷贝数变异和点突变数据,算法能够区分驱动突变与乘客突变对克隆适应度的影响,并量化选择压力强度。
针对表型可塑性建模,开发了基于隐马尔可夫模型的细胞状态转移概率矩阵。该模型通过整合转录因子调控网络和染色质可及性数据,识别关键状态转换节点。特别关注肿瘤干细胞样状态与分化状态间的双向转换机制,引入Waddington景观势能理论量化微环境信号(如TGF-β、WNT等)对状态稳定性的调控作用。模型通过随机微分方程模拟噪声驱动下的状态跃迁过程,解释治疗压力下出现的非遗传性耐药表型。
微环境互作模块采用空间约束的Lotka-Volterra竞争模型,将免疫编辑过程量化为克隆适应度景观的动态重塑。通过空间转录组数据校准免疫细胞亚群的局部分布密度,构建基于配体-受体的细胞通讯网络。模型创新性地引入”生态位抢占”参数,描述特定克隆如何通过分泌特定细胞因子(如VEGF、IL-6等)重塑微环境以获取选择优势。算法通过耦合偏微分方程求解器,模拟免疫细胞浸润与克隆空间扩张的反馈环路。
模型验证采用迭代优化策略,首先在乳腺癌患者来源类器官培养系统中进行单细胞时序追踪实验,通过CRISPR条形码技术标记初始克隆,在不同治疗条件下采集时间序列样本。将实验观测到的克隆频率变化与模型预测进行拟合,结果显示在早期时间点(72小时内)的预测准确率显著优于传统中性演化模型。针对免疫编辑过程的验证则采用人源化小鼠模型,通过流式细胞术定量不同时间点肿瘤浸润免疫细胞组成,证实模型对CD8+ T细胞耗竭动态的预测能力。
技术实现层面,模型采用多层抽象架构设计,底层为C++编写的高性能计算核心,中间层通过Python接口实现模块化参数配置,顶层提供R/Shiny交互式可视化界面。为处理大规模单细胞数据集,开发了基于Spark的分布式计算方案,显著提升万级细胞样本的分析效率。模型支持多种数据输入格式,包括10x Genomics、Smart-seq2等主流单细胞平台输出,并能与TCGA等批量测序数据整合分析。
该模型的创新性体现在三方面:一是首次将克隆系统发育与表型可塑性纳入统一框架,克服了传统演化模型忽视非遗传机制的局限;二是通过空间约束参数实现微环境互作的量化建模,为理解区域免疫逃逸提供新视角;三是开发了可扩展的算法架构,支持后续引入蛋白质组、代谢组等新数据维度。当前局限主要在于对克隆间协同效应的建模尚不完善,未来将通过引入博弈论框架增强模型对集体入侵等复杂行为的解释力。
第四章 研究结论与未来展望
本研究通过整合多维单细胞组学数据与计算建模,系统揭示了肿瘤异质性演化的多层次调控机制。主要结论可归纳为三点:首先,治疗压力下肿瘤干细胞表型可塑性呈现双向动态特征,WNT/β-catenin和Notch信号通路的协同激活是诱导分化细胞重编程为干细胞样状态的关键驱动因素。其次,克隆选择过程表现出明显的空间异质性,中央缺氧区域富集的克隆亚群通过HIF-1α介导的代谢重编程获得选择优势,而侵袭前沿的克隆则依赖EMT-免疫抑制协同演化策略。最后,微环境互作网络分析揭示,特定髓系细胞亚群通过CCL2-CCR2轴促进肿瘤细胞表型转换,这种细胞间通讯模式在多种实体瘤中呈现保守性特征。
从技术方法学角度,本研究开发的整合分析框架具有三方面创新价值:基于多任务学习的细胞状态识别算法有效降低了批次效应干扰;时空耦合的克隆演化模型首次实现了对遗传与非遗传机制的统一建模;配体-受体网络的动态权重调整策略显著提升了细胞互作预测的准确性。这些方法学进步为解析复杂肿瘤生态系统提供了新工具,在乳腺癌和结直肠癌数据集中的验证表明,模型对治疗响应预测的准确率较传统方法有显著提升。
未来研究需重点突破三个方向:在技术层面,需开发保持原生微环境的空间多组学技术,如整合显微切割与单细胞测序的方法,以精确解析细胞互作的空间约束效应。在分析算法上,应探索基于图神经网络的跨尺度建模方法,同时整合基因组变异、表观调控和细胞生态位信息,构建更具预测性的数字孪生模型。临床应用转化方面,亟需建立标准化的单细胞检测临床路径,重点解决液态活检中稀有细胞捕获、快速分析等技术瓶颈,并开发针对肿瘤可塑性关键节点的联合治疗策略。这些研究方向的推进,将有助于将单细胞尺度的基础发现转化为可操作的临床干预靶点,最终实现基于肿瘤异质性动态监测的精准治疗。
参考文献
[1] 王渊.单细胞转录组测序技术在亚实性结节型肺腺癌发生发展机制中的研究进展[J].《临床内科杂志》,2025年第1期86-88,共3页
[2] 胡非凡.单细胞转录组测序技术在胃癌肿瘤微环境重编程研究中的应用进展[J].《南京医科大学学报(自然科学版)》,2025年第2期285-290,共6页
[3] 张洁.单细胞测序在缺血再灌注领域的研究进展[J].《中山大学学报(医学科学版)》,2025年第1期1-10,共10页
[4] 石红雨.单细胞转录组测序技术在结核病研究中的应用[J].《中国防痨杂志》,2025年第3期362-368,共7页
[5] 曹秀蓉.单细胞RNA测序解析子宫内膜异位症血管生成机制[J].《国际妇产科学杂志》,2025年第2期199-205,共7页
通过本文的写作指南与范文解析,相信您已掌握医学毕业论文的核心框架与创新路径。科学严谨的论证逻辑与规范格式的灵活运用,万能小in AI论文应用将助力每位医学生打造兼具学术深度与实践价值的优质论文,为医学研究领域贡献专业力量。



